GIST, 차세대 DNA 저장 기술 개발…"꿈의 저장 기술 현실로 성큼"
국내 연구진이 반영구적이며, 유지 비용도 적게 드는 '데옥시리보핵산' 기반 저장방식을 개발해 차세대 메모리 기술로 주목받고 있다.
기존의 PCR, 혼성화 캡처 등 DNA 파일 접근 기술은 특정 DNA를 증폭하거나 물리적으로 분리하기 위해 서로 다른 프라이머를 설계해야 해 프라이머 설계·합성 비용이 기하급수적으로 증가한다.
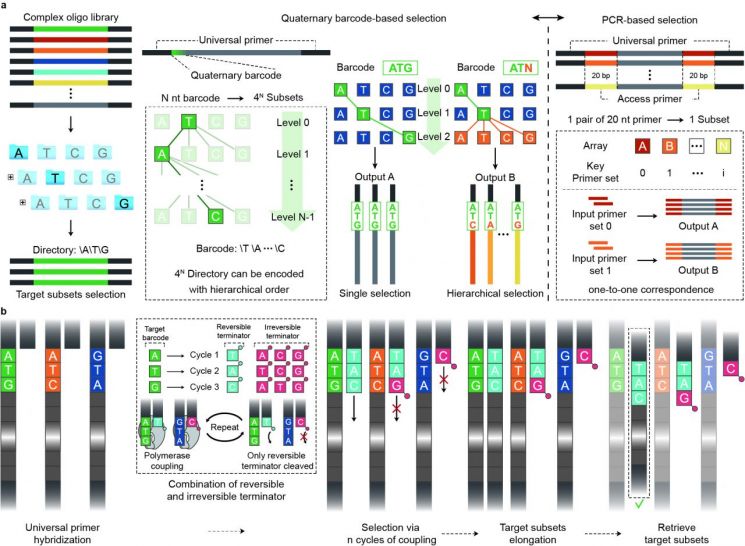
연구팀이 개발한 '순환적 DNA 합성 및 선택' 기술은 단일 염기 수준의 바코드를 활용해 프라이머 없이도 DNA 파일을 계층 구조로 탐색할 수 있도록 설계됐다.
데이터 센터 수준의 저장 효율 및 확장성 확보 가능
프라이머 없이도 4000억 개 이상 DNA 파일에 자유자재 접근
국내 연구진이 반영구적이며, 유지 비용도 적게 드는 '데옥시리보핵산(Deoxyribo Nucleic Acid·DNA)' 기반 저장방식을 개발해 차세대 메모리 기술로 주목받고 있다.
DNA는 대부분의 생명체(일부 바이러스 제외)의 유전 정보를 담고 있는 화학 물질의 일종으로, 전 세계적으로 DNA 응용 기술 연구가 활발히 진행되고 있다.
광주과학기술원(GIST·지스트)은 최영재 신소재공학과 교수 연구팀이 권성훈 서울대학교 교수, ㈜에이티지라이프텍 연구팀과 공동으로 '순환적 DNA 합성 및 선택' 방식을 개발했다고 25일 밝혔다.
순환적 DNA 합성 및 선택(Cyclic DNA Synthesis and Selection) 방식은 특정 DNA 서열을 선택하기 위해 DNA 합성과 선택 과정을 반복적으로 수행하는 방식이다. 이를 통해 DNA 복제나 증폭 과정에서 특정 부분을 찾아주는 프라이머 없이 원하는 특정 DNA 서열만 선택해 남길 수 있게 됐다.
기존의 PCR(polymerase chain reaction), 혼성화 캡처(Hybridization Capture) 등 DNA 파일 접근 기술은 특정 DNA를 증폭하거나 물리적으로 분리하기 위해 서로 다른 프라이머를 설계해야 해 프라이머 설계·합성 비용이 기하급수적으로 증가한다.
연구팀이 개발한 '순환적 DNA 합성 및 선택' 기술은 단일 염기 수준의 바코드를 활용해 프라이머 없이도 DNA 파일을 계층 구조(계층적 선택 방식)로 탐색할 수 있도록 설계됐다.
이는 컴퓨터의 폴더 탐색 방식과 유사한 개념으로, 기존 PCR 방식 대비 비용이 10배 절감되고 접근 효율은 3배 이상 향상됐다. 구분할 수 있는 DNA 파일의 수는 최소 7400만 배 이상 증가했으며, 특정 DNA 파일을 제거하고 새로운 DNA 파일을 삽입하는 등 파일 교체도 가능해졌다.
기존 PCR 방식에서는 DNA 파일마다 별도의 프라이머(최소 20개 염기) 한 쌍을 설계하고 합성해야 했지만, 이 기술은 4개의 염기만으로 특정 DNA 파일에 접근할 수 있다.
이 기술을 활용하면 DNA 데이터 내 특정 파일을 보다 정밀하게 찾아내고 자유자재로 조작할 수 있다. 기존 실리콘 반도체 메모리의 한계를 뛰어넘어 데이터 집적도를 '데이터 센터' 수준까지 획기적으로 높일 수 있을 것으로 기대되는 이유다.
최영재 교수는 "이번 연구를 통해 프라이머 없이도 특정 DNA 파일에 접근할 수 있는 새로운 방법론을 제시해 계층적 바코드 시스템을 적용함으로써 기존 PCR 방식의 한계를 극복했다"면서 "향후 바코드 설계 최적화 및 자동화된 시스템과 결합하면 차세대 DNA 파일 접근 기술로서 DNA 기반 저장 시스템 상용화에 중요한 돌파구가 될 것으로 기대한다"고 설명했다.
꼭 봐야 할 주요 뉴스
 "편의점·술집·모텔 어디든 다 뚫는다"…수십만원...
"편의점·술집·모텔 어디든 다 뚫는다"…수십만원...
이번 연구는 GIST 신소재공학과 최영재 교수가 지도하고 김우진 석박통합과정생과 고윤혜 석사과정생이 함께 수행했으며, 과학기술정보통신부 STEAM연구사업(미래유망융합기술파이오니어)의 지원을 받았다. 연구 결과는 국제학술지 '네이처 커뮤니케이션즈(Nature Communications)'에 지난 12일 온라인 게재됐다.
<ⓒ투자가를 위한 경제콘텐츠 플랫폼, 아시아경제(www.asiae.co.kr) 무단전재 배포금지>








![[기자수첩]베이징에서 사라진 아반떼…현대차는 다시 달릴 수 있을까](https://cwcontent.asiae.co.kr/asiaresize/308/2026042810544432006A.jpg)
![[시시비비]1910조원의 경고, '풍선효과'보다 무서운 '부동산 침몰'](https://cwcontent.asiae.co.kr/asiaresize/308/2026042808311189657A.jpg)
![[초동시각]사각지대 선 '핀플루언서'...사후규제 한계 커](https://cwcontent.asiae.co.kr/asiaresize/308/2026042811071987057A.jpg)







![올해 첫 'SK하이닉스 투자의견 하향' 보고서 등장…"하반기 성장성 약화"[클릭 e종목]](https://cwcontent.asiae.co.kr/asiaresize/308/2024102515542673983_1729839265.jpg)





![[속보] 김정관 산업장관 "삼성전자 이익, 노사만의 몫인가…공동체 고려해야"](https://cwcontent.asiae.co.kr/asiaresize/309/2026041415271425588_1776148034.jpg)


![[단독]AI 신약 난제 풀리나…효능·생산성 동시에 잡았다](https://cwcontent.asiae.co.kr/asiaresize/309/2026042807451642590_1777329916.png)